基于ubuntu系统的AutoDock-Vina的分子对接实操教程(极简版)
前言
传统的体外实验方法,如紫外-可见光谱(UV-vis)、荧光光谱、圆二色谱(CD)、电化学方法以及表面等离子体共振(SPR)传感器,长期以来一直被用于研究生物活性化合物的相互作用机制。然而,它们无法直接揭示原子水平上的相互作用。
分子模拟方法能够准确、直观地在原子层面预测结合模式,揭示体外实验难以捕捉的机制细节。它们还能辅助更高效地重新设计功能大分子,并从包含数百万分子的大型数据库中快速筛选生物活性化合物。
目标与意义
- 掌握分子对接的流程
- 学会最常见的蛋白-小分子对接任务
分子对接的流程
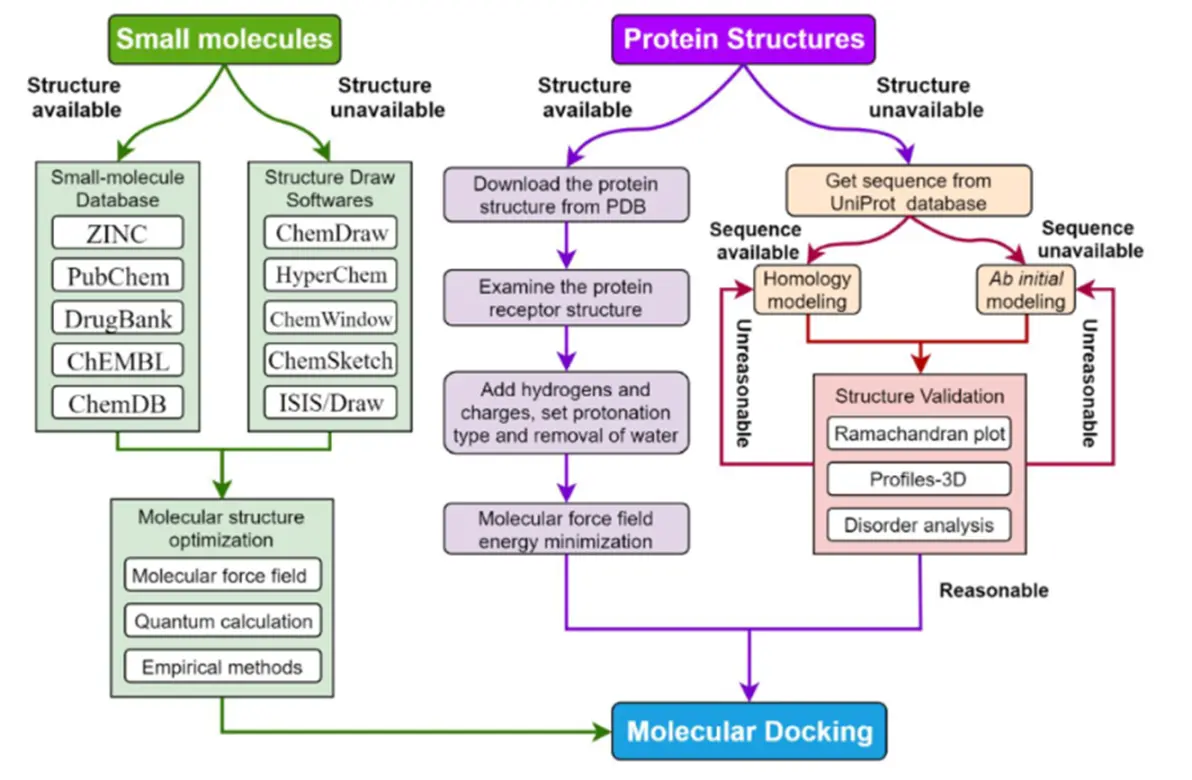
Yu Y, Xu S, He R, et al. Application of molecular simulation methods in food science: Status and prospects[J]. Journal of agricultural and food chemistry, 2023, 71(6): 2684-2703.
分子对接的实操
本次分子对接所做的任务是蛋白结构与小分子结构皆已知的对接
对接对象:人胰脂肪酶 x 奥利司他
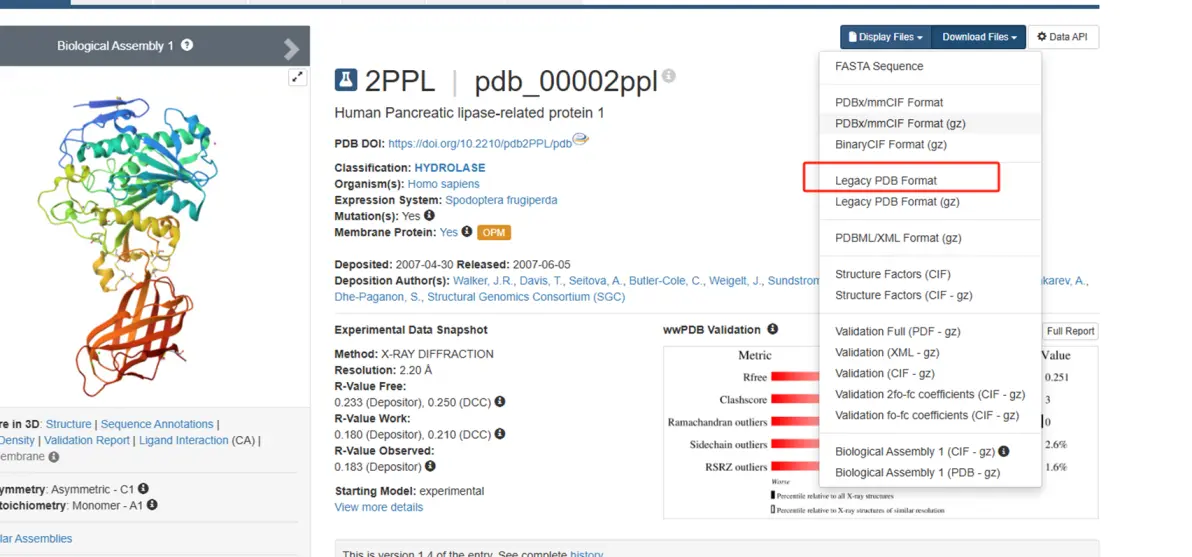
对接受体的下载与处理
RCSB 中搜集人胰脂肪酶的三维结构(PDB)
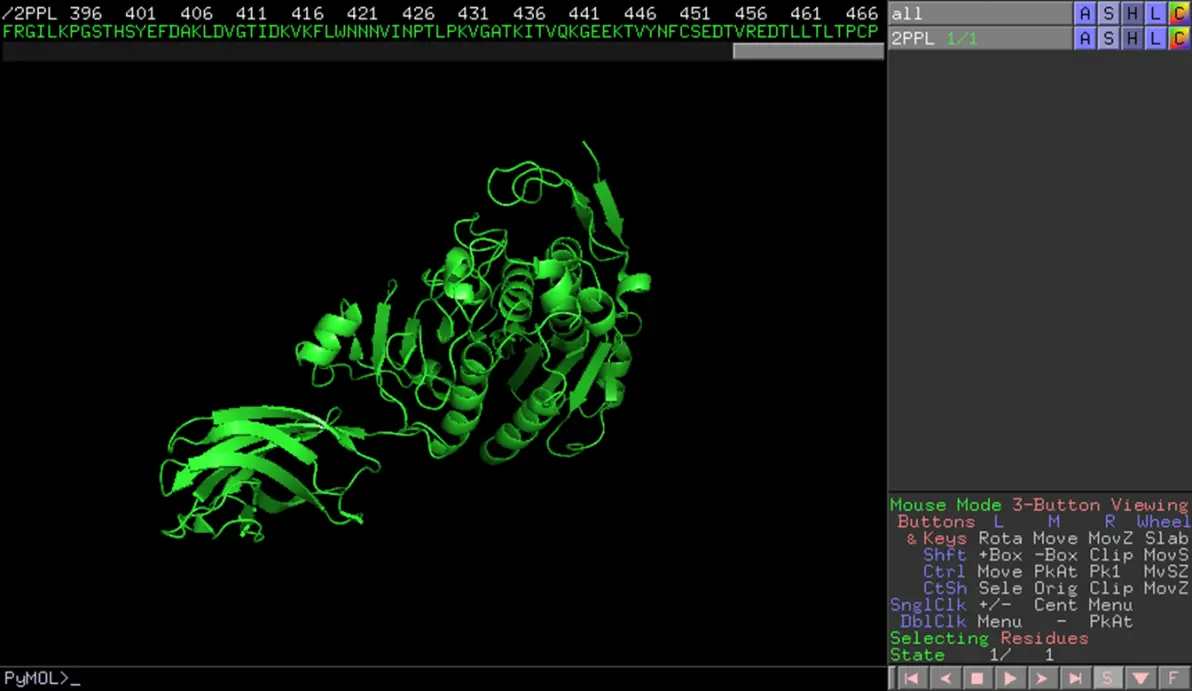
使用 Pymol 对胰脂肪酶进行处理(去水加氢)
使用 p2Rank 预测胰脂肪酶对接位点
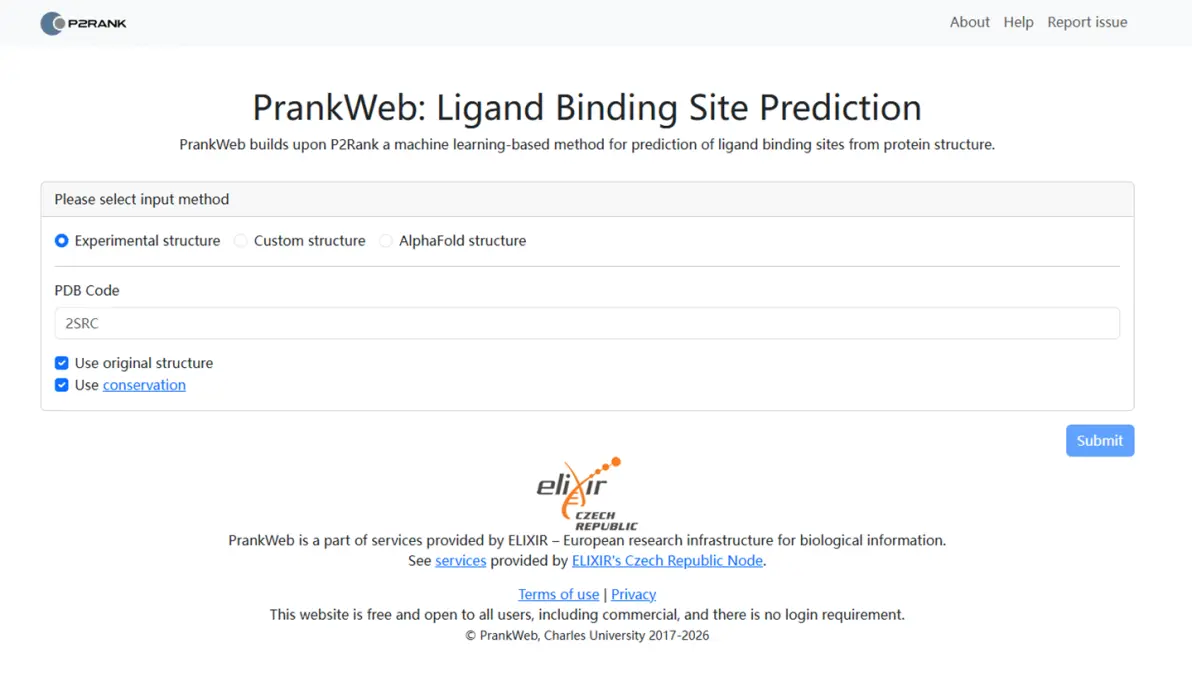
center_x、center_y、center_z 是本次对接所需的对接位点
对接配体的下载与处理
使用 pubchem 下载奥利司他小分子(Mol2)
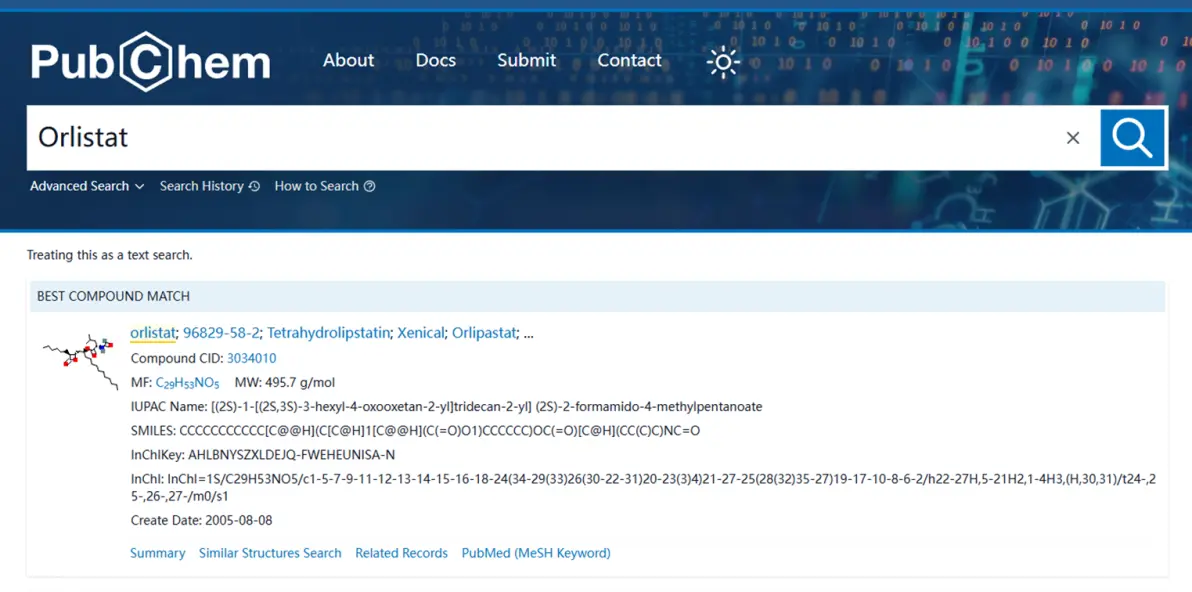
使用 pymol 处理奥利司他小分子(加氢)
若有需求,需要对小分子做能量最小化(高斯、orca)
编写对接配置文件
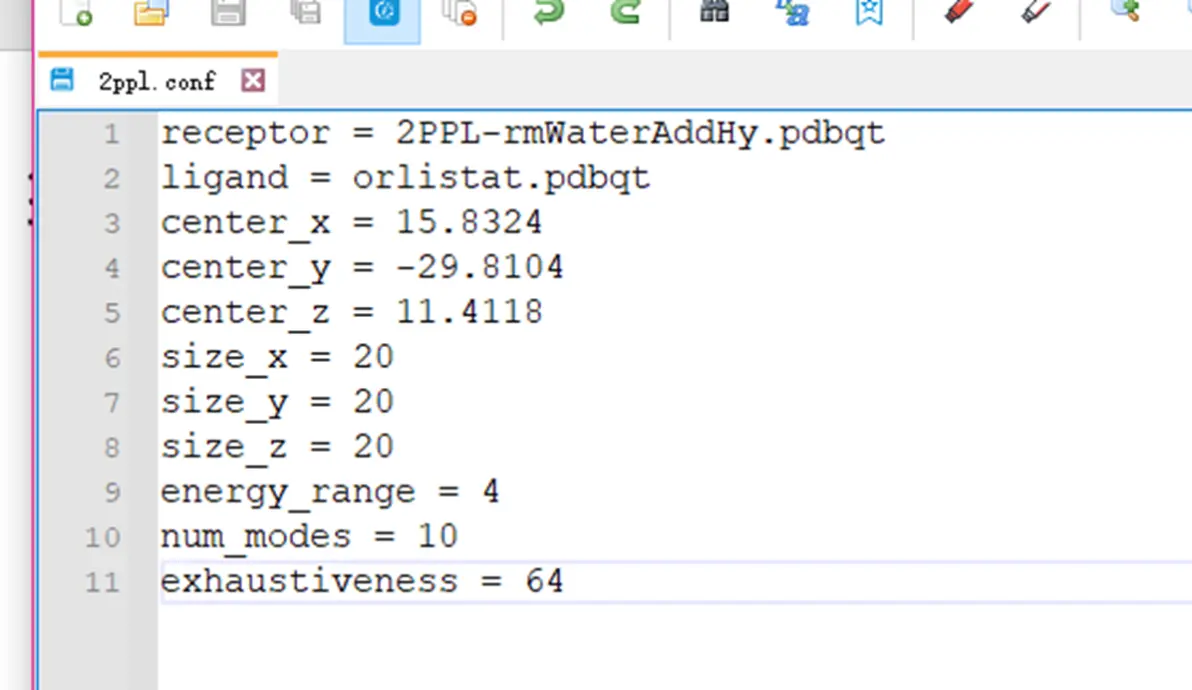
对接文件格式转换(pdb、mol2 转换为 pdbqt)
进入 ubuntu 系统,安装 mgltools 并配置好 python 解释器
在 ubuntu 下输入命令进行文件格式的转换,以便 Vina 识别三维结构文件
1 | 受体文件的格式转换命令 |
转换格式完毕后,在 ubuntu 下安装 autodock-vina 并运行对接命令
1 | 安装autodock-vina |
运行完毕后,会生成含结合能的对接结果以及对接后的小分子配体,该结果可用于后续的分子动力学模拟
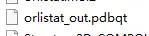
分子对接结果文件